Chemischer Werkzeugkasten ermöglicht neue Einblicke in Proteine
- Top-Meldungen
- Forschung

Die Emmy Noether-Nachwuchsgruppe von Dr. Malte Gersch von der Fakultät für Chemie und Chemische Biologie hat einen chemischen Werkzeugkasten entwickelt, der Einblicke in die Wirkweise des speziellen Proteins Fubi ermöglicht. Ihre Erkenntnisse haben die Wissenschaftler*innen kürzlich in der renommierten Fachzeitschrift Nature Chemical Biology veröffentlicht.
Das kleine Protein Ubiquitin ist besonders dafür bekannt, andere Proteine für deren Abbau zu markieren, und wirkt dadurch in der Regulation aller zellulären Prozesse mit. Durch diese Markierung wird beispielsweise verhindert, dass sich fehlerhafte oder nicht mehr benötigte Proteine in den Zellen anreichern. Parallel zum Ubiquitin-System existieren verschiedene andere Ubiquitin-ähnliche Proteine, von denen Fubi trotz seiner immun-modulatorischen Aktivität nur wenig untersucht ist. Fubi wird in Fusion mit dem ribosomalen Protein S30 hergestellt. Damit die Ribosomen – die Proteinfabriken der Zelle – funktionieren, muss Fubi von S30 abgetrennt werden.
Einblicke in die Wirkweise des Proteins
Immunzellen nutzen dieses Nebenprodukt der Ribosom-Herstellung als Signalprotein, um beispielsweise in der Gebärmutter die Aktivität des mütterlichen Immunsystems lokal abzusenken und damit die Einnistung von Embryonen zu ermöglichen. Wie Fubi spezifisch von Proteasen zur Abtrennung von S30 erkannt wird und wie sich Fubi von Ubiquitin unterscheidet, war bisher nicht bekannt.
Wissenschaftler*innen um Dr. Malte Gersch, der die an der Fakultät für Chemie und Chemische Biologie sowie am Chemical Genomics Center des Max-Planck-Instituts für molekulare Physiologie angesiedelte Emmy Noether-Nachwuchsgruppe leitet, haben nun erste molekulare Einblicke in den Mechanismus gewonnen, der die Fubi-kontrollierte Reifung des Schlüsselproteins S30 ermöglicht.
„Werkzeugkasten“ fördert Verständnis von Fubi-System
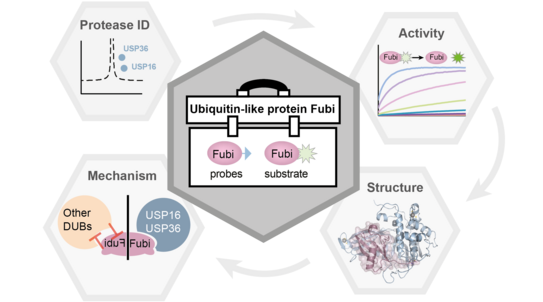
Mithilfe eines neu entwickelten chemischen Werkzeugkastens konnten die Forscher*innen auf molekularer Ebene feststellen, wie die zwei deubiquitinierenden Enzyme USP16 und USP36 über eine weitere spezifische Fubi-Protease-Aktivität verfügen. Diese doppelte Fubi-/Ubiquitin-Spezifität erlaubt die Fubi-S30-Maturierung in zwei räumlich bestimmten Umgebungen der Zelle und verhindert zugleich, dass die große Anzahl der weiteren nur Ubiquitin-spezifischen Enzyme Fubi prozessieren.
„Unsere Ergebnisse zeigen die molekulare Verschränkung des Ubiquitin-Systems mit dem bisher wenig erforschten Fubi-System. Zusammen mit dem von uns entwickelten chemisch-biologischen Werkzeugkasten wird dies auch das Verständnis von Fubi als Protein-Modifikation in zellulären Prozessen erweitern“, sagt Dr. Malte Gersch.
Ansprechpartner für Rückfragen:




















